基因功能注释包下载、制作与富集分析
关于基因功能富集分析的教程之前其实介绍过很多,比较简单的方法是直接使用在线工具(如OmicShare tools)去完成币安钱包下载。如果是使用R语言,我觉得对初学者来说比较“凌乱”的是相关注释包的下载安装。
闲言少叙,下面就以具体的例子看下,如何安装基因功能富集分析相关的R包并完成简单的GO、KEGG富集分析币安钱包下载。本文的主要内容是clusterProfiler相关R包的安装、GO、KEGG富集分析、尝试自己创建目标物种的kegg注释包等。
1. 安装所需的R包
#选择Bioconductor的国内镜像;
chooseBioCmirror
#5: China (Peking)
#6: China (Nanjing)
#安装"BiocManager"包;
install.packages( "BiocManager")
library(BiocManager)
#安装富集分析所需的注释包(这里仅是人的);
install( "GO.db")
install( "org.Hs.eg.db")
#安装clusterProfiler包;
install( "clusterProfiler")
#安装作图包;
展开全文
install( "enrichplot")
#载入所需的R包;
library(GO.db)
library(org.Hs.eg.db)
library(clusterProfiler)
library(enrichplot)
library(ggplot2)
2. 载入范例数据
#设置工作目录;
setwd( "C:/Users/币安钱包下载你自己的文件位置/范例数据")
#读入目的gene数据;
df<-read.table( "ensembl.txt",sep = "\t",header= T)
#准备目的gene列表;
genelist<-unique(as.vector(df[,1]))
genelist[1:12]
#GO富集分析;
#sub ontology这里选"MF“,也可以分别选"BP","CC"或"ALL";
#这里的geneid类型选"ENSEMBL";
go<- enrichGO(genelist, OrgDb = org.Hs.eg.db,
ont='MF',
pAdjustMethod= 'BH',
pvalueCutoff= 0.05,
qvalueCutoff= 0.2,
keyType= 'ENSEMBL')
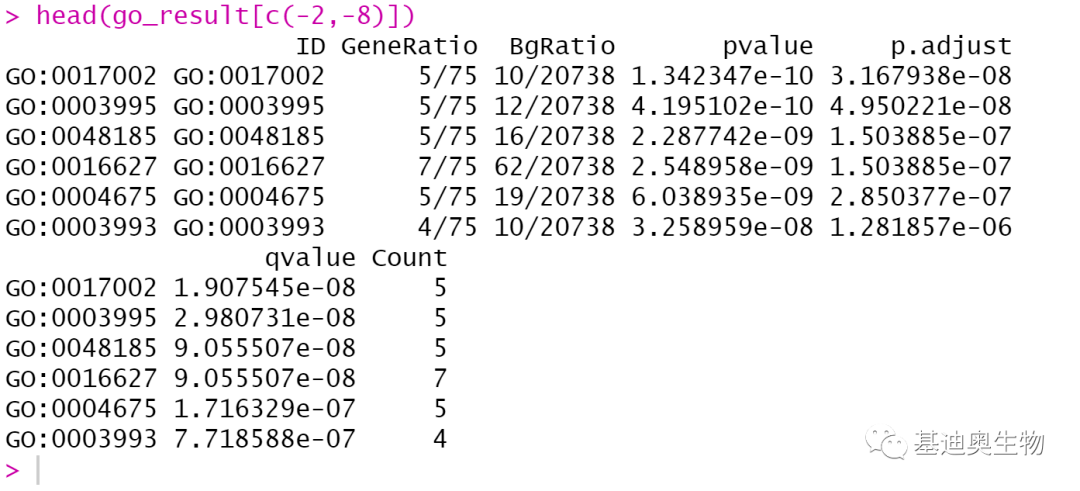
#查看GO富集结果;
go_result<-go@result
head(go_result[c(-2,-8)])
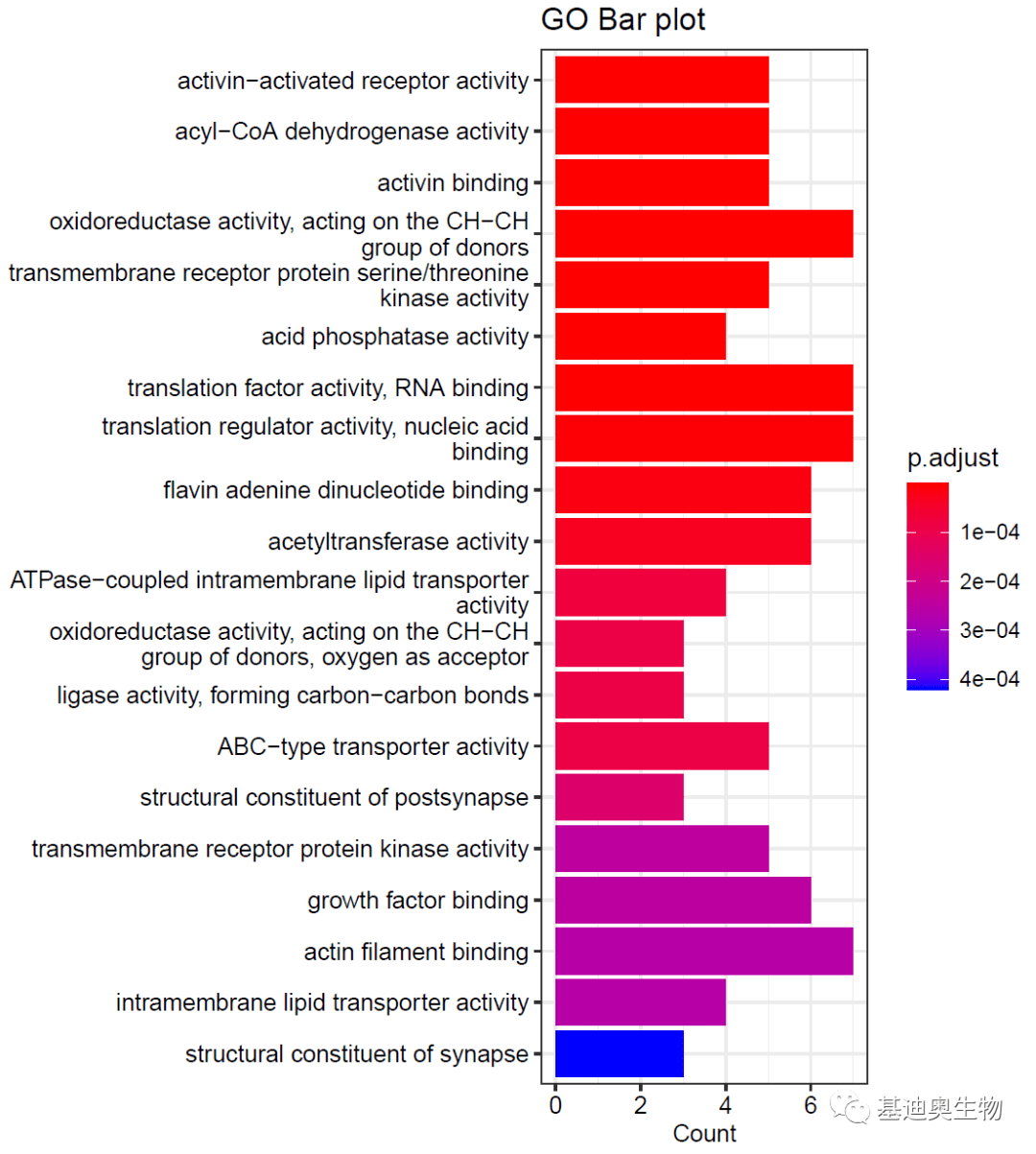
#绘制条形图;
#label_format表示文字标签的换行字符数;
#showCategory展示分类标签的数量;
p1<-barplot(go, font.size = 10,
title= "GO Bar plot",
label_format= 50,
showCategory=20)
p1
#绘制气泡图;
p2<-dotplot(go, font.size = 10,
title= "GO Dot plot",
label_format= 50,
showCategory=20)
p2

#使用ggplot2包做个性化调整;
#设置x轴范围币安钱包下载,避免点的溢出绘图区;
p3<-p2+scale_x_continuous(limits = c(0.025, 0.1),
breaks= c(0.025,0.05,0.075, 0.10),
label= c( "0.025", "0.05", "0.075", "0.10"))
p3

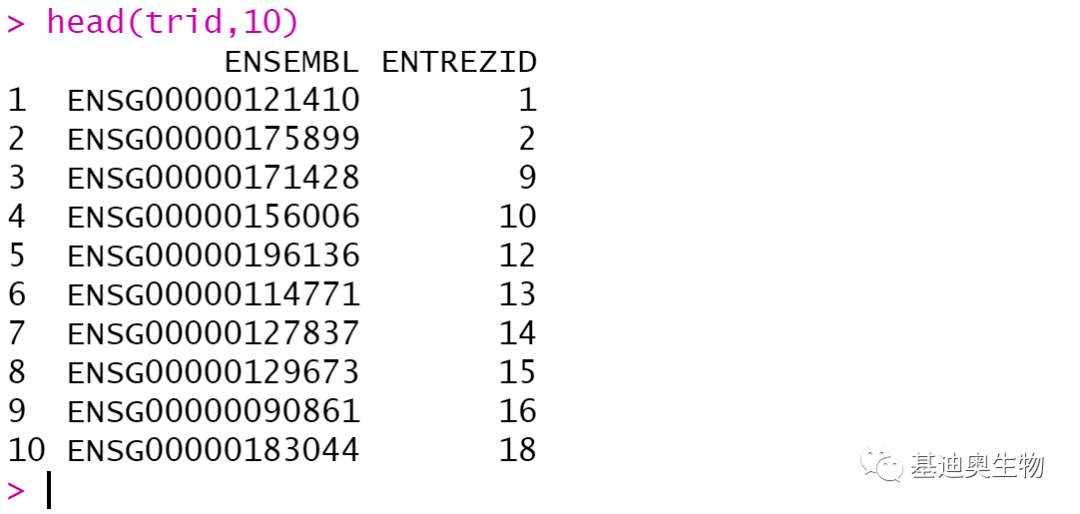
#geneid转换:
#将"ENSEMBL ID"转换成"ENTREZ ID";
trid<- bitr(genelist, fromType= "ENSEMBL",
toType=c( "ENTREZID"),
OrgDb= "org.Hs.eg.db")
head(trid,10)
#提取转换成gene id;
genelist2<-as.vector(trid$ENTREZID)
#线上下载方法设置;
install.packages( "R.utils")
R.utils::setOption( "clusterProfiler.download.method",'auto')
#KEGG富集分析;
#使用online KEGG 注释信息进行富集分析(需要一点点时间);
kegg<- enrichKEGG(genelist2, organism = 'hsa',
keyType= 'kegg',
pvalueCutoff= 0.05,
pAdjustMethod= 'BH',
qvalueCutoff= 0.2,
use_internal_data= F)
#查看kegg富集结果;
kegg_result<-kegg@result
head(kegg_result[c(-2,-8)])
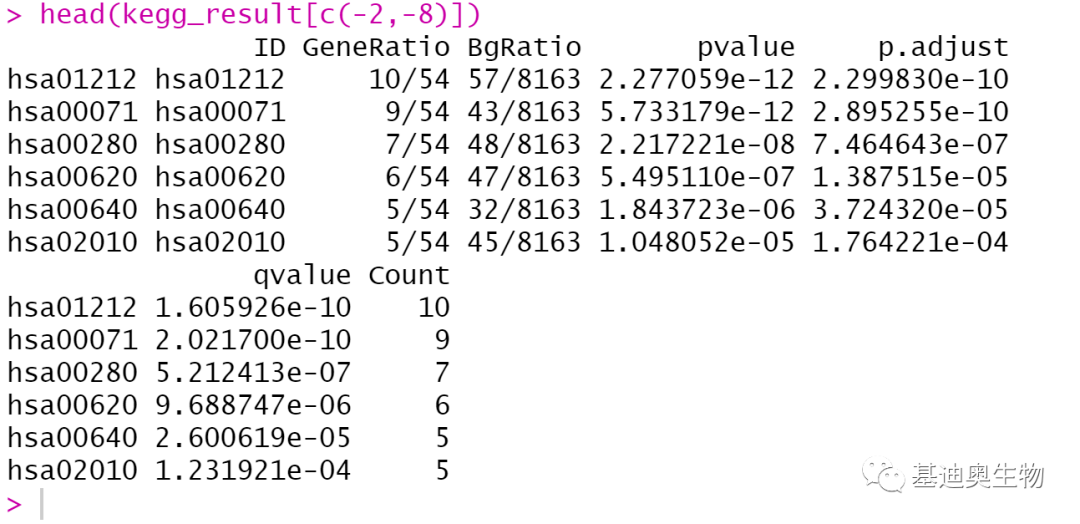
#绘制KEGG气泡图;
p4<-dotplot(kegg,font.size = 10,
title= "KEGG Dot plot",
label_format= 50,
showCategory=20)
p4
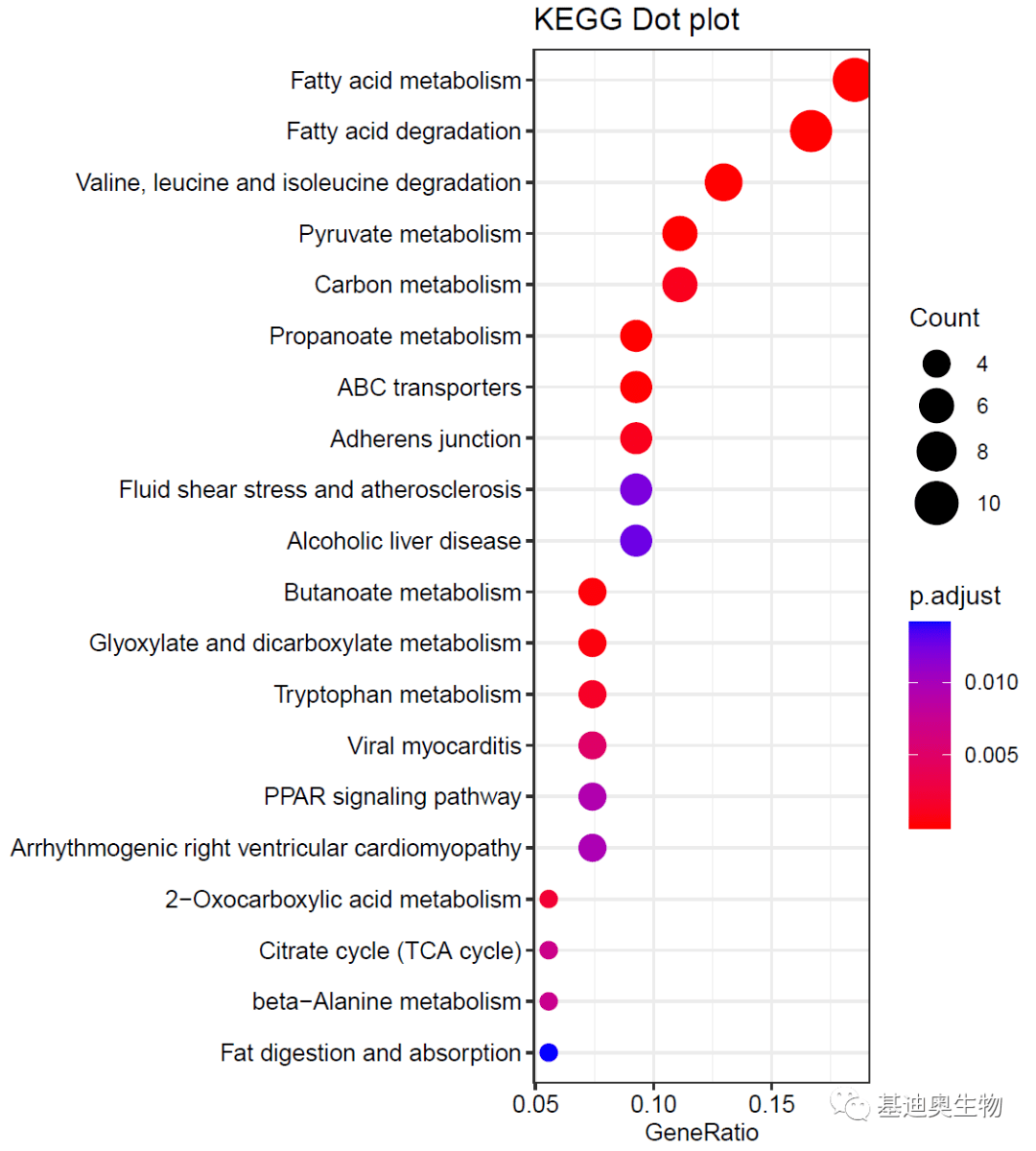
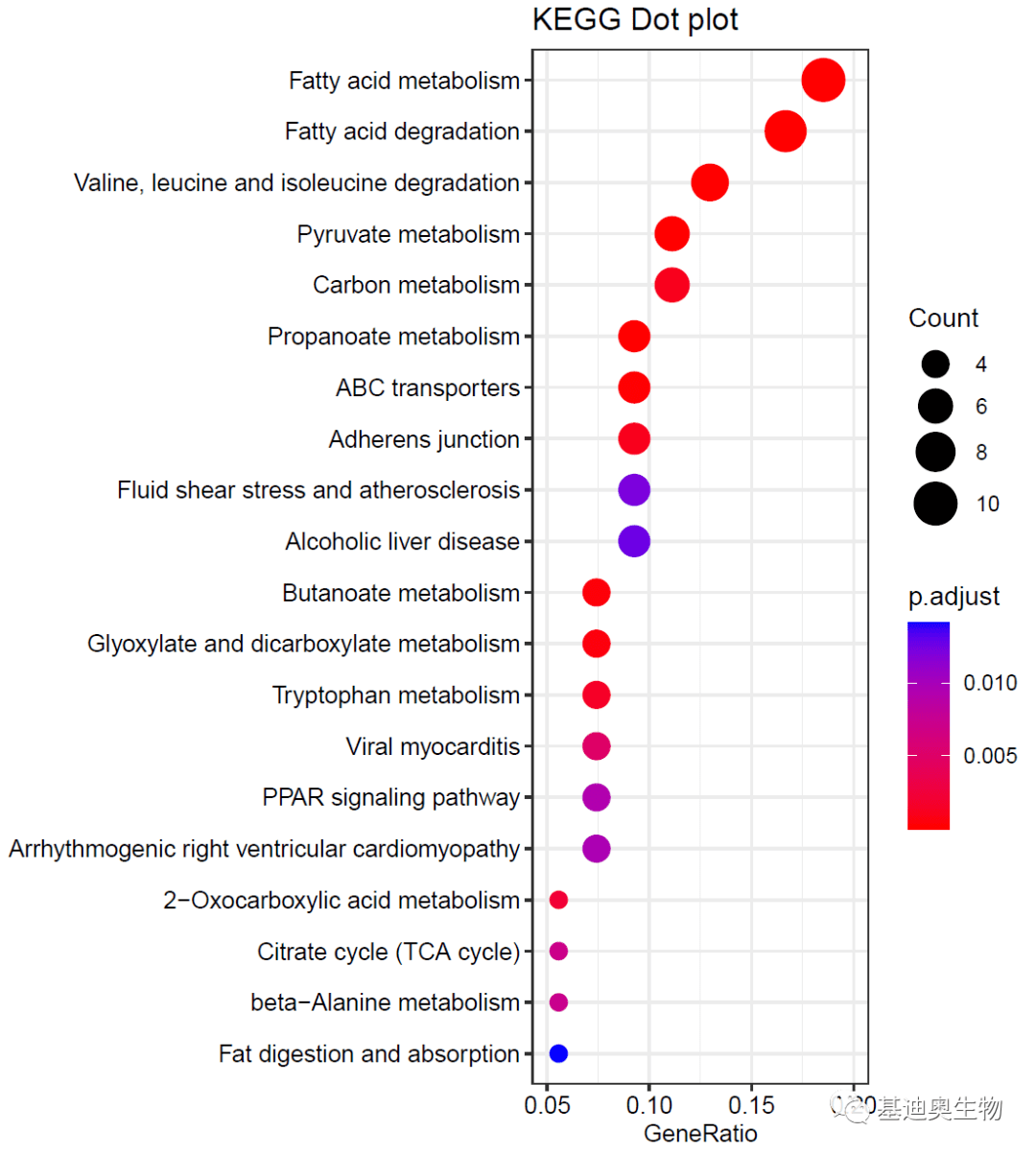
#设置x轴范围币安钱包下载,避免点的溢出绘图区;
p5<-p4+scale_x_continuous(limits = c(0.05, 0.2),
breaks= c(0.05,0.10,0.15, 0.20),
label= c( "0.05", "0.10", "0.15", "0.20"))
p5
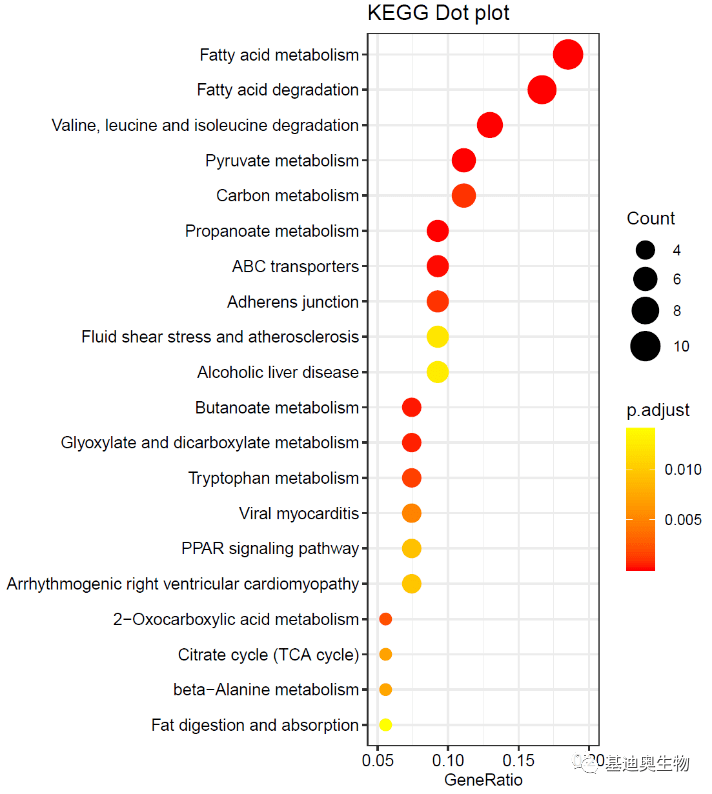
#自定义渐变颜色;
p6<-p5+scale_colour_gradient(low= "red",high= "yellow")
p6
3. 自己创建kegg注释包
#安装createKEGGdb包;
install.packages( "remotes")
remotes::install_github( "YuLab-SMU/createKEGGdb")
#创建感兴趣物种的本地kegg.db包;
library(createKEGGdb)
指定需要下载的物种,比如,玉米("zma",Zea mays)、拟南芥("ath",Arabidopsis thaliana)、酵母("sce",Saccharomyces cerevisiae)、人("hsa",Homo sapiens)、小鼠("mmu",Mus musculus)、斑马鱼("dre", Danio rerio)等;更多的物种对应关系可以到查看币安钱包下载。
#币安钱包下载我这里选择创建几个常见物种的kegg注释包;
species<-c( "hsa", "mmu", "ath", "zma", "sce", "dre")
create_kegg_db(species)

#当前工作目录中会自动创建名称为KEGG.db_1.0.tar.gz的源码包;
#当然也可仅创建自己关注物种的注释包;
#create_kegg_db('zma')
#或者创建KEGG上所有物种的注释包;
#create_kegg_db("all")
#安装自己创建的源码R包;
#repos=NULL表示本地安装;
install.packages( "~/KEGG.db_1.0.tar.gz",
repos=NULL,type= "source")
#载入自己创建的KEGG.db包;
library(KEGG.db)
#使用本地数据(KEGG.db)进行富集分析;
res_hsa<- enrichKEGG(gene = genelist2,
organism= 'hsa',
pvalueCutoff= 0.05,
qvalueCutoff= 0.05,
use_internal_data= T)
#预览富集分析结果;
head(res_hsa)

#浏览感兴趣的通路图;
browseKEGG(res_hsa, 'hsa04110')
好啦币安钱包下载,本次的分享就到这里啦!
参考资料
/
*未经许可,不得以任何方式复制或抄袭本篇文章之部分或全部内容币安钱包下载。版权所有,侵权必究。
如果你还在为不知如何绘制SCI图表而忧愁币安钱包下载,还在为毕业论文制图效率低下而焦心,或者想要找到一个生信学习、绘图软件学习、R语言学习的干货集中地……
关注一个SCIPainter就对了!什么叫大隐隐于市币安钱包下载,什么叫酒香巷子深,什么叫少林寺的扫地僧!怀揣绘图绝技,深藏功名的就是它!SCIPainter!!!
SCIPainter是基迪奥旗下的科研图表类干货分享公众号币安钱包下载,之后更多与科研图表绘制相关内容,我们会在这个账号中持续进行分享和发布,聪明的你一定不会错过!
左手一个基迪奥生物币安钱包下载,右手一个SCIPainter,老板再也不用担心我的课题和论文了!
基迪奥生物|专业定制测序服务
联系方式:020-39341079;service@genedenovo.com







评论